-심포지엄 발표를 위한 논문정리-
\Abstract
Naturally occuring protein switches (eg. G protein)에서 착안, peptide key가 binding하면 특정 반응을 일으키는 protein switch를 이용해 biosensor를 설계함. 이 biosensor는 modular, closed dark state와 open luminescent state를 가짐. Analyte binding과 sensor activation이 thermodynamically coupled -> target binding domain 1개 (simple)
본 논문에서는 Bcl-2 (anti-apoptotic protein), IgG1 Fc domain, Her2 receptor, Botulinum neurotoxin B, cardiac troponin I, anti-hepatitis B virus antibody를 감지할 수 있는 biosensor를 제작함.
또한 SARS-CoV-2 spike protein, membrane antibody, nucelocapsid protein에 대한 biosensor도 제작함 (논문 publish 2021년). Spike protein sensor는 15 pM의 detection limit, 50-fold higher signal을 보임.
이 sensor의 modularity와 sensitivity는 여러 analyte에 대한 sensor construction이 가능하게 함.
De novo protein design -> multi-state system을 설계하여 특정 기능을 수행하도록 하는 연구의 중요성.
\Main
기존의 biosensor design은 natural protein을 reengineering하는 수준에 그침.
Analyte-specific하며, binding시 conformational change가 일어나는 domain을 찾는 것 / 이것을 찾아도 reporter domain과 coupling 하는 것이 어렵기 때문.
따라서 traget에 따라 repurpose 가능한 modular (조립식, 모듈로 구성) platform을 구축하는 것이 필요함.
Antibody, small molecule (NAD+ 등)을 감지하는 modular system은 연구되었으나(Banala S. et al., Arts, R. et al., Yu, Q. et al.) protein은 structure, size, oligomerization state 등의 diversity 때문에 어려움. 또한 semisynthetic protein platform, calmodulin switch 등의 approach는 낮은 predictability 때문에 screening 매우 많이 해야함.
Protein biosensor는 2개의 isoenergetic state을 가지는 system으로 구성되며, 이 평형은 analyte binding에 의해 조절.
요구되는 특징으로는
1) analyte의 detail과는 무관하게 conformational change가 일어나서 여러 target sensing이 가능해야 함
2) tunable 해야 함 -> binding energy가 다르거나 typical concentration이 다른 여러 analyte에 대해 적용 가능
3) conformational change가 sensible output과 coupled되어야 함
본 논문에서는 de novo protein switch - target binding이 peptide actuator presence에 의해 조절되는 2-protein system을 사용. (Fig. 1a)
lucCage: cage domain, latch domain (target binding motif와 split luciferase fragement(SmBiT) 포함)
luckey: lucCage의 open state에 binding하는 key peptide, SmBiT에 complementary한 LgBit
lucCage의 closed state: cage domain이 latch에 bind, binding motif-target binding과 SmBiT-LgBit binding 막음
lucCage의 open state: binding interaction이 방해받지 않고 luckey가 cage domain에 binding 가능
luckey - lucCage association은 luciferase activity reconstitution.
free energy (Fig. 1b, c):
target absent condition에서 luckey-lucCage binding << lucCage opening
target present condition에서 latch-target binding + luckey-lucCage binding >> lucCage opening
즉 target present일 때만 opening 일어남
이러한 설계는 위의 성질 3가지를 만족함 - 여러 binding이 cage와 결합될 수 있으며 luckey-target binding energy가 target typical concentration에 맞게 tuned 될 수 있음, luciferase activity로 sensing 가능
luckey, lucCage는 다 똑같이 쓸 수 있음 (modular)
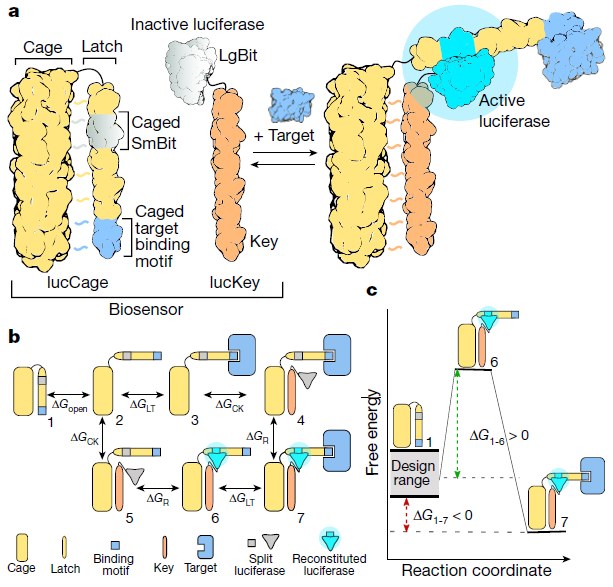
이 system은 thermodynamical equlibrium에 있으며, delta G_open, delta G_cage-key, delta G_latch-target 조절하여 각 species ratio 조절 가능.

위의 parameter와 analyte / sensor component concentration에 따른 luciferase activity
Analyte detection sensitivity는 G_latch-target의 함수(extended Fig. 1b), 약 0.1*K_d(dissociation of latch-target)의 lower limit (그래프 상승 시작 지점)
이 lower limit 이상에서는 lucCage, lukkey concentration 조절하여 target concentration에 맞게 tuning 가능(extended Fig. 1c, d)
G_open과 G_cage-key도 중요, G_open 너무 작으면 background (target absent) signal 커지고 G_cage-key 너무 크면 target 있어도 low signal 등 (extended Fig. 1a, e)
본 논문에서는 latch, key의 helix length를 조절하고 cage-latch, cage-key interface의 amino acid interaction을 조절하여 이 balance를 잡음.
extended Fig. 1 e에서 G 가 크다 <-> K가 작다 <-> 역반응이 favorable <-> lower limit이 더 낮다 이렇게 보면 될듯?
GraftS-witchMover Rosetta-based method: closed state에서 stable하며 target과 interaction이 blocked되는 latch 내의 target binding peptide 배열을 찾기
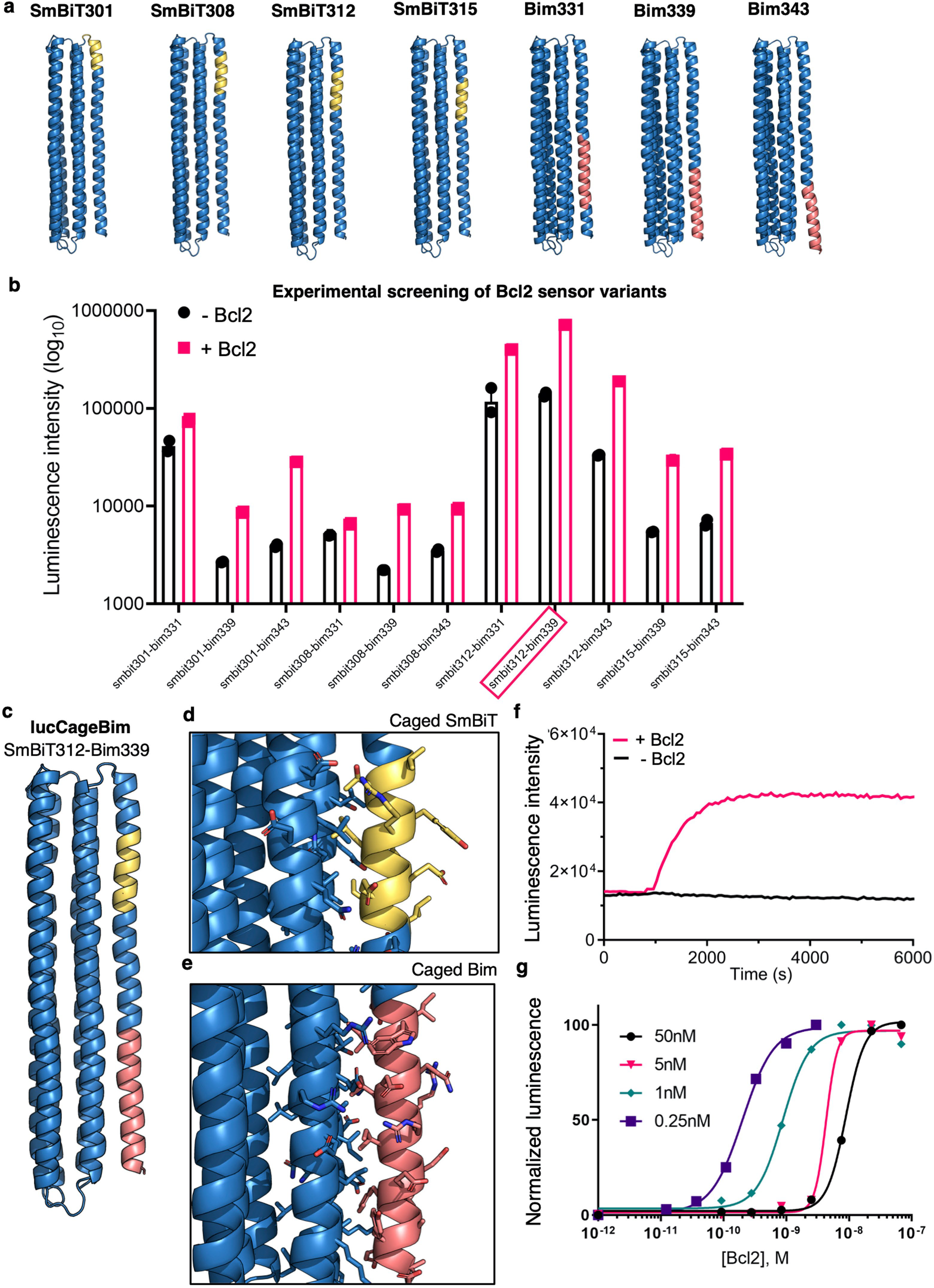
1) SmBiT, BIM peptide in closed state LOCKR switch latch (6주차)
SmBiT는 luciferase holoenzyme에서 beta-strand 구조이지만 LOCKR latch같은 helical structure에서는 helical 구조 가질 것이라 assume (secondary structure can be context dependent)
latch 상에서 SmbiT, BIM 옮겨가며 에너지 확인, lowest energy solution 12종 확인 (extended Fig. 2a)
E.coli에서 express 후 luckey와 1:1로 혼합, BCL-2 (BIM과 nanomolar(K_d=10^-9)하게 bind) 첨가 -> luciferase 확인 (extended Fig. 2b), 이중 best SmBiT-BIM 위치 조합을 lucCageBim이라 명명
즉 <특정 key가 있을 때만 작동하도록 설계된 LOCKR switch를 거꾸로 biosensor로 사용 가능>
Analyte detection range는 sensor (lucCage + luckey) concentration 조절하여 변화 (extended Fig. 2g)
lucCageBim의 SmBiT 위치는 312번째로, 이후 실험에는 이 lucCage를 scaffold로 이용.
(이해되지 않은 모종의 computational 방법 개발)
influenza A H1 haemagglutinin (HA) binding protein을 설계, 이것을 LOCKR의 shortened version (sCAGE)에 삽입
Functional, key 있는 조건에서만 HA bound인 best design (Fig. 2a) 확인.
이 경우 HA-binding interface가 Phe273 빼고 전부 cage domain과 interact하여 key absent 시 latch to HA binding을 (as intended) 잘 막고 있었음
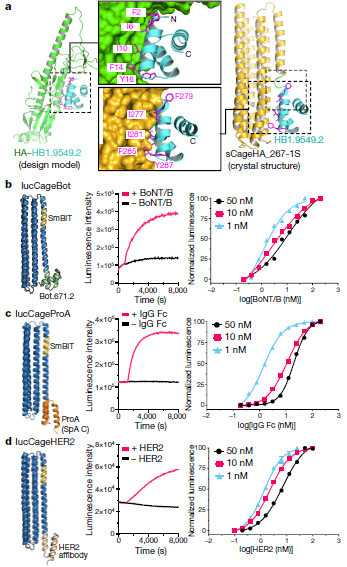
이 computational method로 Botulinum neurotoxin B (BoNT/B), Ig Fc domain, HER2 receptor에 대한 sensor 개발.
후보 몇 가지에 대한 screening 진행하여 각 target에 대한 highly sensitive lucCage 개발, Fig. 2 b, c, d와 같이 target addition 후 몇 분만에 luminescence 확인. lucCage, luckey concentration 조절하여 sensitivity tuning 가능.
-> Food industry에서 rapid / low-cost Bot detection, serological HER2 level detection 등에 이용 가능.
lucCage sensor for cardiac troponin
cardiac torponin 1: standard early diagnostic biomarker for acute myocardial infarction (급성 심근경색)
cardiac troponin T, C, 1 (cTnT, cTnC, cTn1) 간의 high affinity interaction을 이용, 6개의 truncated cTnT sequence를 latch에 여기저기 넣어보면서 11개의 후보 정함, best 선택 (lucCageTrop627)
acute myocardial infarction patient rule-in /rule-out level은 picomolar 한데 이 sensor의 detection range는 이정도로 낮지 않음
앞에서 (Fig. 1) 조사했듯 limit of detection ~ 0.1K_d (latch-target)이므로 lucCageTrop627의 cTn1 affinity를 높여 LOD를 낮추려고 함.
cTnC를 sensor의 C-terminus에 fusion시켜서 cTnT, cTnC, cTn1 간의 high affinity interaction을 이용.
결과물인 lucCageTrop은 clinical sample 처리에 용이한 LOD를 가짐 (Fig. 3 b, extended Fig. 6 e, f)

lucCage sensor for hepatitis B (HBV), SARS-CoV-2 antibodies
antibody monitoring: population 내 pathogen spreading, vaccination succes, therapeutic antibody 추적
lucCage에 antibody가 인식하는 linear epitope를 lucCage에 incorporate.
*linear epitope: aa sequence 상에서 continuous <-> conformational epitope: aa sequence 상에서는 discontinuous하나 3D 구조상에서는 proximity
Target: antibody against HBV surface protein L의 preS1 domain
8 candidates, best design lucCageHBV -> 150 % increase in luciferase activity after anti-HBV Ab addition
dynamic range (max lumi / min lumi), LOD 개선하기 위한 lucCageHBValpha: bivalent antibody - latch affinity 높이기 위해 epitope 하나 더 붙임
-> LOD 260 pM, dynamic range 225 % (Fig. 3e)
Serological level of therapeutic antibodies ~ nanomolar range 이므로 이 platform은 효과적.
HBV surface sensor 제작: sensor-antibody complex가 HBV surface protein preS1 presence에서는 dissociate하고 antibody는 HBV와 binding할 것 (Fig. 3f)
실제로 preS1 addition 후 lumi 줄어듬 (Fig. 3g).
anti-HBV antibody 농도를 조절하여 preS1의 post-HBV infection level (Fig. 3h grey)내의 detection 가능
lucCage sensor for SARS-CoV-2 antibodies
SARS-CoV (=SARS-CoV-1, 사스 원인), SARS-CoV-2 proteome에서 highly immunogenic하고, 다른 Coronaviridae(과)에는 없는 linear epitope identify.
이중 SARS, COVID-19 patient sera에서 recognized된 membrane(M), nucleocapsid(N) protein
M epitope, N epitope, anti-M, anti-N antibody를 specific하게 recognize하는 sensor design(Ex fig 8).
2-5분만에 full signal 도달했으며 LOD는 low nanomolar, dynamic range는 50-70 % (Fig. 4a, b)

'Biology' 카테고리의 다른 글
| Modelling neural network as matrix (0) | 2024.08.29 |
|---|---|
| 20240826 Neural circuit basis of placebo pain relief (0) | 2024.08.27 |